Haplogrupa L3 (mtDNA) - Haplogroup L3 (mtDNA)
| Haplogrupa L3 | |
|---|---|
| Możliwy czas powstania | 80 000–60 000 YBP |
| Możliwe miejsce pochodzenia | Afryka Wschodnia czy Azja |
| Przodek | L3'4 |
| Potomków | L3a, L3b'f, L3c'd, L3e'i'k'x, L3h, M , N |
| Definiowanie mutacji | 769, 1018, 16311 |
Haplogrupa L3 jest człowiek mitochondrialnego DNA (mtDNA) Haplogrupa . Klad odegrał kluczową rolę we wczesnym rozproszeniu anatomicznie współczesnych ludzi .
Jest silnie związany z migracją współczesnych ludzi poza Afrykę sprzed około 70–50 000 lat. Jest dziedziczony przez wszystkie współczesne populacje nieafrykańskie, a także przez niektóre populacje w Afryce.
Początek

Haplogrupa L3 powstała blisko 70 000 lat temu, w czasie niedawnego wydarzenia poza Afryką . To rozproszenie powstało w Afryce Wschodniej i rozszerzyło się na Azję Zachodnią, a następnie na Azję Południową i Południowo-Wschodnią w ciągu kilku tysiącleci, a niektóre badania sugerują, że L3 uczestniczyła w tej migracji z Afryki. Szacunki z 2007 roku dotyczące wieku L3 sugerowały przedział 104–84 000 lat temu. Nowsze analizy, w tym Soares et al. (2012) dochodzą do nowszej daty, około 70–60 000 lat temu. Soares i in. sugerują również, że L3 najprawdopodobniej rozszerzyła się z Afryki Wschodniej do Eurazji około 65-55 000 lat temu w ramach niedawnego wydarzenia poza Afryką, a także z Afryki Wschodniej do Afryki Środkowej przed 60-35 000 lat temu. W 2016 roku Soares i in. ponownie zasugerował, że haplogrupa L3 pojawiła się w Afryce Wschodniej, prowadząc do migracji poza Afrykę, około 70-60 000 lat temu.
Haplogrupy L6 i L4 tworzą siostrzane klady L3, które powstały w Afryce Wschodniej mniej więcej w tym samym czasie, ale które nie uczestniczyły w migracji poza Afrykę. Pierwotny klad L3'4'6 został oszacowany na około 110 kya, a klad L3'4 na 95 kya.
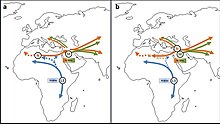
Możliwość pochodzenia L3 z Azji zaproponowali również Cabrera i in. (2018) na podstawie podobnych dat koalescencji L3 i jego kladów pochodnych M i N w euroazjatyckim rozkładzie (ok. 70 kya), odległej lokalizacji w Azji Południowo-Wschodniej najstarszych znanych subkladów M i N oraz porównywalnego wieku haplogrupa ojcowska DE . Zgodnie z tą hipotezą, po początkowej migracji poza Afrykę nosicieli pre-L3 (L3'4*) około 125 kya, miałaby miejsce migracja wsteczna samic niosących L3 z Eurazji do Afryki Wschodniej około 70 lat. kya. Hipoteza sugeruje, że ta migracja powrotna jest wyrównana z nosicielami ojcowskiej haplogrupy E , która również sugeruje, że pochodzi z Eurazji. Sugeruje się, że te nowe linie eurazjatyckie w dużej mierze zastąpiły stare autochtoniczne męskie i żeńskie linie rodowe z Afryki północno-wschodniej.
Według innych badań, chociaż miały miejsce wcześniejsze migracje z Afryki anatomicznie współczesnych ludzi, obecne populacje euroazjatyckie wywodzą się z późniejszej migracji z Afryki, datowanej między około 65 000 a 50 000 lat temu (związanej z migracją z L3).
Vai i in. (2019) sugerują, z nowo odkrytej starej i głęboko zakorzenionej gałęzi matczynej haplogrupy N znalezionej we wczesnych neolitycznych szczątkach północnoafrykańskich, że haplogrupa L3 pochodzi z Afryki Wschodniej między 70 000-60 000 lat temu i zarówno rozprzestrzeniła się w Afryce, jak i opuściła Afrykę w ramach migracji poza Afrykę, z haplogrupą N odchodzącą od niej wkrótce (między 65 000-50 000 lat temu) w Arabii lub prawdopodobnie w Afryce Północnej, a haplogrupa M pochodząca z Bliskiego Wschodu mniej więcej w tym samym czasie co N.
Badanie przeprowadzone przez Lipsona i in. (2019) analiza szczątków z kameruńskiego stanowiska Shum Laka wykazała, że są one bardziej podobne do współczesnych ludów Pigmejów niż do mieszkańców Afryki Zachodniej i sugeruje, że kilka innych grup (w tym przodkowie mieszkańców Afryki Zachodniej, Afryki Wschodniej i przodkowie nie -Afrykanie) powszechnie wywodzące się z populacji ludzkiej pochodzącej z Afryki Wschodniej między około 80 000-60 000 lat temu, co, jak sugerują, było również źródłem i strefą pochodzenia haplogrupy L3 około 70 000 lat temu.
Dystrybucja
L3 jest powszechne w Afryce Północno-Wschodniej i niektórych innych częściach Afryki Wschodniej, w przeciwieństwie do innych części Afryki, gdzie haplogrupy L1 i L2 stanowią około dwóch trzecich linii mtDNA. Na Półwyspie Arabskim często występują również sublinie L3 .
L3 dzieli się na kilka kladów, z których dwa dały początek makrohaplogrupom M i N, które są obecnie noszone przez większość ludzi poza Afryką. Istnieje co najmniej jedna stosunkowo głęboka nie-M, nie-N klad L3 poza Afryką, L3f1b6, który występuje z częstością 1% w Asturii w Hiszpanii. Oddzieliła się od afrykańskich linii L3 co najmniej 10 000 lat temu.
Według Maca-Meyera i in. (2001), „L3 jest bardziej związana z haplogrupami euroazjatyckimi niż z najbardziej rozbieżnymi afrykańskimi klastrami L1 i L2 ”. L3 to haplogrupa, z której wywodzą się wszyscy współcześni ludzie poza Afryką. Jednak istnieje większa różnorodność głównych gałęzi L3 w Afryce niż poza nią, przy czym dwie główne nieafrykańskie gałęzie to odgałęzienia L3 M i N.
Dystrybucja podkladu
L3 ma siedmiu równoodległych potomków: L3a, L3b'f, L3c'd, L3e'i'k'x, L3h, M, N. Pięć jest afrykańskich, a dwóch jest związanych ze zdarzeniem Out of Africa .
- N – Eurazja prawdopodobnie z powodu migracji z Afryki, a Afryka Północna prawdopodobnie z powodu migracji wstecznej z Eurazji.
- M – Azja , basen Morza Śródziemnego i części Afryki z powodu migracji powrotnej.
-
L3a – Afryka Wschodnia. Umiarkowane do wysokich częstotliwościach występujących pomiędzy Sanye , Samburu , Iraqw , Yaaku , El-Molo i innych drobnych rdzennej ludności z African Rift Valley East . Rzadko nie istnieje w Sudanie i strefie Sahelu.
- L3a1 – Znajduje się w całej Afryce Wschodniej. Szacowany wiek 35,8–39,3 tys.
- L3a2 – Znajduje się w całej Afryce Wschodniej. Szacowany wiek 48,3–57,7 tys.
-
L3b'f
-
L3b – Rozprzestrzenianie się od Afryki Wschodniej w górnym paleolicie do Afryki Zachodnio-Środkowej. Niektóre subklady rozprzestrzeniły się z Afryki Środkowej do Afryki Wschodniej wraz z migracją Bantu.
-
L3b1a – Wspólna podklada . Szacowany wiek 11,7-14,8 tys.
- L3b1a2 – Subklad znaleziony w północno-wschodniej Afryce, Maghrebie i na Bliskim Wschodzie. Pojawiły się 12–14 tys.
-
L3b1a – Wspólna podklada . Szacowany wiek 11,7-14,8 tys.
-
L3f – Afryka Północno-Wschodnia, Sahel, Półwysep Arabski, Iberia. Gaalien , Beja
-
L3f1
- L3f1a – Przewożony przez migrantów z Afryki Wschodniej do Sahelu i Afryki Środkowej.
-
L3f1b – Przewożony przez migrantów z Afryki Wschodniej do Sahelu i Afryki Środkowej.
-
L3f1b1 – Przeniesiony z Afryki Środkowej do Afryki Południowej i Wschodniej wraz z migracją Bantu.
- L3f1b1a –
-
L3f1b1 – Przeniesiony z Afryki Środkowej do Afryki Południowej i Wschodniej wraz z migracją Bantu.
- L3f1b4 – Przeniesiony z Afryki Środkowej do Afryki Południowej i Wschodniej wraz z migracją Bantu.
-
L3f1
- L3f1b6 – Rzadki, znaleziony w Iberii.
-
L3b – Rozprzestrzenianie się od Afryki Wschodniej w górnym paleolicie do Afryki Zachodnio-Środkowej. Niektóre subklady rozprzestrzeniły się z Afryki Środkowej do Afryki Wschodniej wraz z migracją Bantu.
- L3f2 – Rozprowadzany głównie w Afryce Wschodniej. Występuje również w Afryce Północnej i Afryce Środkowej.
- L3f3 – Rozprzestrzenił się z Afryki Wschodniej do Czadu i Sahelu około 8-9 ka. Znaleziony w dorzeczu Czadu .
- L3c – Niezwykle rzadki rodowód z zaledwie dwoma próbkami znalezionymi do tej pory w Afryce Wschodniej i na Bliskim Wschodzie .
-
L3d – Rozprzestrzenianie się od Afryki Wschodniej w górnym paleolicie do Afryki Środkowej. Niektóre subklady rozprzestrzeniły się do Afryki Wschodniej wraz z migracją Bantu. Znaleziono wśród Fulani , Czadu , Etiopczycy , Akan ludzi , Mozambik , Yemenites , Egipcjan , Berberów
- L3d3a1 – Znajdowany głównie w Afryce Południowej.
-
L3e – Rozprzestrzenianie się od Afryki Wschodniej w górnym paleolicie do Afryki Zachodnio-Środkowej. Jest to najczęstszy podklad L3 w populacjach mówiących w języku Bantu . Sugeruje się, że L3e ma pochodzenie z Afryki Środkowej i jest również najczęstszym podkladem L3 wśród Afroamerykanów, Afro-Brazylijczyków i Karaibów
- L3e1 – Rozprzestrzenianie się z Afryki Zachodnio-Środkowej do Afryki Południowo-Zachodniej wraz z migracją Bantu. Znaleziono w Angoli (6,8%). Mozambik, Sudańczyk i Kikuju z Kenii, a także w Jemenie i wśród ludu Akan
- L3e5 – Pochodzi z dorzecza Czadu. Występuje w Algierii , Burkina Faso , Nigerii , Południowej Tunezji , Południowym Maroku i Egipcie
-
L3i Prawie wyłącznie w Afryce Wschodniej.
-
L3i1
- L3i1b – Subclade występuje w Jemenie, Etiopii i wśród Indian Gujarati.
- L3i2 (dawniej L3w) – znaleziony w Rogu Afryki i Omanie.
-
L3i1
- L3k – Rzadka haplogrupa występująca głównie w Afryce Północnej i Sahelu.
- L3x – prawie wyłącznie w Afryce Wschodniej. Znaleziony wśród etiopskich Oromos , Egipcjan
- L3h1 – Występuje głównie w Afryce Wschodniej z gałęziami L3h1b1 sporadycznie spotykanymi w Sahelu i Afryce Północnej.
- L3h2 – Znaleziony w północno-wschodniej Afryce i Socotra. Oddzielił się od innych gałęzi L3h już w 65-69 ka w środkowym paleolicie .
Próbki starożytne i historyczne
Haplogrupa L3 została zaobserwowana w starożytnej skamieniałości należącej do kultury B z okresu przed-garncarskiego neolitu . L3x2a zaobserwowano u 4500-letniego łowcy-zbieracza wykopanego w Mota w Etiopii, przy czym starożytna skamielina okazała się najściślej spokrewniona ze współczesnymi populacjami południowo-zachodniej Etiopii . Haplogrupa L3 stwierdzono także wśród starożytnych egipskich mumii (1/90; 1%) wykopanych w Abusir el-Meleq archeologicznego w Środkowym Egipcie, z resztą wynikającą z Eurazji subclades, które pochodzą z Pre Ptolemejskiego / koniec Nowego Państwa i okresy ptolemejskie. Starożytne egipskie mumie zawierały bliskowschodni komponent genomowy, który jest najbliżej spokrewniony ze współczesnymi mieszkańcami Bliskiego Wschodu. Dodatkowo haplogrupę L3 zaobserwowano w starożytnych skamielinach Guanche wykopanych na Gran Canarii i Teneryfie na Wyspach Kanaryjskich , które zostały datowane radiowęglowo na okres między VII a XI wiekiem naszej ery. Wszystkie osobniki niosące klad były inhumowane na stanowisku Gran Canaria, przy czym większość tych okazów należała do podkladu L3b1a (3/4; 75%), a reszta pochodziła z obu wysp (8/11; 72%) z subkladów euroazjatyckich. Szkielety Guanczów zawierały również autochtoniczny składnik genomu Maghrebi , który jest szczytem wśród współczesnych Berberów , co sugeruje , że pochodzą one z rdzennych populacji Berberów zamieszkujących północno-zachodnie Affoundnat o wysokiej ncy .
Różnorodność L3 została odkryta w starożytnych szczątkach związanych z pasterskim neolitem i pasterską epoką żelaza we wschodniej Afryce.
| Kultura | Klaster genetyczny lub powinowactwo | Kraj | Strona | Data | Haplogrupa matczyna | Haplogrupa ojcowska | Źródło |
| Wczesne duszpasterskie | PN | Kenia | Wąwóz Prettejohna (GsJi11) | 4060–3860 | L3f1b | – | Prendergast 2019 |
| Neolit duszpasterski | PN | Kenia | Pogrzeb Cole'a (GrJj5a) | 3350–3180 | L3i2 | E-V32 | Prendergast 2019 |
| Neolit duszpasterski lub Elmenteitan | PN | Kenia | Jaskinia Rigo (GrJh3) | 2710–2380 | L3f | E-M293 | Prendergast 2019 |
| Neolit duszpasterski | PN | Kenia | Schronisko Naishi | 2750–2500 | L3x1a | E-V1515 (prob. E-M293) | Prendergast 2019 |
| Neolit duszpasterski | PN | Tanzania | Jaskinia Gishimangeda | 2490-2350 | L3x1 | – | Prendergast 2019 |
| Neolit duszpasterski | PN | Kenia | Miejsce pochówku Naivasha | 2350-2210 | L3h1a1 | E-M293 | Prendergast 2019 |
| Neolit duszpasterski | PN | Kenia | Miejsce pochówku Naivasha | 2320–2150 | L3x1a | E-M293 | Prendergast 2019 |
| Neolit duszpasterski | PN | Tanzania | Jaskinia Gishimangeda | 2150-2020 | L3i2 | E-M293 | Prendergast 2019 |
| Neolit duszpasterski lub Elmenteitan | PN | Kenia | Jaskinia rzeki Njoro II | 2110-1930 | L3h1a2a1 | – | Prendergast 2019 |
| Neolit duszpasterski | Nie dotyczy | Tanzania | Jaskinia Gishimangeda | 2000-1900 | L3h1a2a1 | – | Prendergast 2019 |
| Neolit duszpasterski | PN | Kenia | Ol Kalou | 1810–1620 | L3d1d | E-M293 | Prendergast 2019 |
| Duszpasterska epoka żelaza | PIA | Kenia | Farma Kisima, C4 | 1060-940 | L3h1a1 | E-M75 (bez M98) | Prendergast 2019 |
| Duszpasterska epoka żelaza | PIA | Kenia | Emurua Ole Polos (GvJh122) | 420–160 | L3h1a1 | E-M293 | Prendergast 2019 |
| Duszpasterska epoka żelaza | wartość odstająca PN | Kenia | Kokurmatakore | Nie dotyczy | L3a2a | E-M35 (nie E-M293) | Prendergast 2019 |
Drzewo
To drzewo filogenetyczne podkladów haplogrupy L3 jest oparte na pracy Mannisa van Ovena i Manfreda Kaysera. Zaktualizowane kompleksowe drzewo filogenetyczne globalnej zmienności ludzkiego mitochondrialnego DNA i późniejsze opublikowane badania.
Najnowszy wspólny przodek (MRCA)
- L1-6
- L2-6
- L2'3'4'6
- L3'4'6
- L3'4
-
L3
- L3a
- L3a1
- L3a1a
- L3a1b
- L3a2
- L3a2a
- L3a1
- L3b'f
- L3b
- L3b1
- L3b1a
- L3b1a1
- L3b1a2
- L3b1a3
- L3b1a4
- L3b1a5
- L3b1a5a
- L3b1a6
- L3b1a7
- L3b1a7
- L3b1a8
- L3b1a9
- L3b1a9a
- L3b1a10
- L3b1a11
- L3b1b
- L3b1b1
- L3b1a
- L3b2
- L3b2a
- L3b2a
- L3b3
- L3b1
- L3f
- L3f1
- L3f1a
- L3f1a1
- L3f1b
- L3f1b1
- L3f1b2
- L3f1b2a
- L3f1b3
- L3f1b4
- L3f1b4a
- L3f1b4a1
- L3f1b4b
- L3f1b4c
- L3f1b4a
- L3f1b5
- L3f1a
- L3f2
- L3f2a
- L3f2b
- L3f3
- L3f3a
- L3f3b
- L3f1
- L3b
- L3c'd
- L3c
- L3d
- L3d1-5
- L3d1
- L3d1a
- L3d1a1
- L3d1a1a
- L3d1a1
- L3d1b
- L3d1b1
- L3d1c
- L3d1d
- L3d1a
- 199
- L3d2
- L3d5
- L3d3
- L3d3a
- L3d4
- L3d5
- L3d1
- L3d1-5
- L3e'i'k'x
- L3e
- L3e1
- L3e1a
- L3e1a1
- L3e1a1a
- 152
- L3e1a2
- L3e1a3
- L3e1a1
- L3e1b
- L3e1c
- L3e1d
- L3e1e
- L3e1a
- L3e2
- L3e2a
- L3e2a1
- L3e2a1a
- L3e2a1b
- L3e2a1b1
- L3e2a1
- L3e2b
- L3e2b1
- L3e2b1a
- L3e2b2
- L3e2b3
- L3e2b1
- L3e2a
- L3e3'4'5
- L3e3'4
- L3e3
- L3e3a
- L3e3b
- L3e3b1
- L3e4
- L3e3
- L3e5
- L3e3'4
- L3e1
- L3i
- L3i1
- L3i1a
- L3i1b
- L3i2
- L3i1
- L3k
- L3k1
- L3x
- L3x1
- L3x1a
- L3x1a1
- L3x1a2
- L3x1b
- L3x1a
- L3x2
- L3x2a
- L3x2a1
- L3x2a1a
- L3x2a1
- L3x2b
- L3x2a
- L3x1
- L3e
- L3h
- L3h1
- L3h1a
- L3h1a1
- L3h1a2
- L3h1a2a
- L3h1a2b
- L3h1b
- L3h1b1
- L3h1b1a
- L3h1b1a1
- L3h1b1a
- L3h1b2
- L3h1b1
- L3h1a
- L3h2
- L3h1
- m
- n
- L3a
-
L3
- L3'4
- L3'4'6
- L2'3'4'6
- L2-6
Zobacz też
|
Drzewo filogenetyczne haplogrup ludzkiego mitochondrialnego DNA (mtDNA) |
|||||||||||||||||||||||||||||||||||||||
| Ewa mitochondrialna ( L ) | |||||||||||||||||||||||||||||||||||||||
| L0 | L1–6 | ||||||||||||||||||||||||||||||||||||||
| L1 | L2 | L3 | L4 | L5 | L6 | ||||||||||||||||||||||||||||||||||
| m | n | ||||||||||||||||||||||||||||||||||||||
| CZ | D | mi | g | Q | O | A | S | r | i | W | x | Tak | |||||||||||||||||||||||||||
| C | Z | b | F | R0 | przed JT | P | U | ||||||||||||||||||||||||||||||||
| HV | JT | K | |||||||||||||||||||||||||||||||||||||
| h | V | J | T | ||||||||||||||||||||||||||||||||||||
Bibliografia
Uwagi
Zewnętrzne linki
- Ogólny
- Miejsce mitochondrialnego DNA Iana Logana
- Haplogrupa L3
- Mannis van Oven's PhyloTree.org – poddrzewo mtDNA L3
- Rozprzestrzenianie się Haplogrupy L3 , z National Geographic



