Pyrosequencing - Pyrosequencing
Pirosekwencjonowanie jest metodą sekwencjonowania DNA (określania kolejności nukleotydów w DNA) opartą na zasadzie „sekwencjonowania przez syntezę”, w której sekwencjonowanie przeprowadza się poprzez wykrycie nukleotydu włączonego przez polimerazę DNA . Pirosekwencjonowanie polega na wykrywaniu światła w oparciu o reakcję łańcuchową, w której uwalnia się pirofosforan . Stąd nazwa pyrosequencing.
Zasada pirosekwencjonowania została po raz pierwszy opisana w 1993 roku przez Bertila Petterssona , Mathiasa Uhlena i Pål Nyrena poprzez połączenie metody sekwencjonowania w fazie stałej z użyciem kulek magnetycznych pokrytych streptawidyną z rekombinowaną polimerazą DNA pozbawioną aktywności 3–5 „eksonukleazy (odczyt dowodowy) i detekcją luminescencji przy użyciu enzymu lucyferazy świetlika . Mieszanina trzech enzymów ( polimerazy DNA , sulfurylazy ATP i lucyferazy świetlika ) i nukleotydu ( dNTP ) dodaje się do jednoniciowego DNA, który ma być zsekwencjonowany, a po włączeniu nukleotydu mierzy się emitowane światło. Intensywność światła określa, czy włączono 0, 1 lub więcej nukleotydów, pokazując w ten sposób, ile komplementarnych nukleotydów jest obecnych na nici matrycowej. Mieszaninę nukleotydów usuwa się przed dodaniem następnej mieszaniny nukleotydów. Proces ten powtarza się dla każdego z czterech nukleotydów, aż do określenia sekwencji DNA jednoniciowej matrycy.
Druga metoda pirosekwencjonowania oparta na rozwiązaniach została opisana w 1998 roku przez Mostafę Ronaghi , Mathiasa Uhlena i Påla Nyrena . W tej alternatywnej metodzie wprowadza się dodatkowy enzym apyrazę w celu usunięcia nukleotydów, które nie są włączone przez polimerazę DNA. Umożliwiło to dodanie mieszaniny enzymów zawierającej polimerazę DNA , lucyferazę i apyrazę na początku i utrzymanie jej przez całą procedurę, zapewniając w ten sposób prostą konfigurację odpowiednią do automatyzacji. Zautomatyzowany instrument oparty na tej zasadzie został wprowadzony na rynek w następnym roku przez firmę Pyrosequencing.
Trzeci wariant mikrofluidyczny metody Pyrosequencing został opisany w 2005 roku przez Jonathana Rothberga i współpracowników z firmy 454 Life Sciences . To alternatywne podejście do pirosekwencjonowania oparto na oryginalnym zasadę mocowania do sekwencjonowania DNA do stałego nośnika, i wykazano, że kolejność działań może być przeprowadzane w sposób bardzo równolegle stosując mikroukład mikromacierzy . Pozwoliło to na wysokoprzepustowe sekwencjonowanie DNA i zautomatyzowany instrument został wprowadzony na rynek. Stało się to pierwszym instrumentem do sekwencjonowania nowej generacji, rozpoczynającym nową erę w badaniach genomiki , z szybko spadającymi cenami sekwencjonowania DNA, umożliwiającymi sekwencjonowanie całego genomu po przystępnych cenach.
Procedura
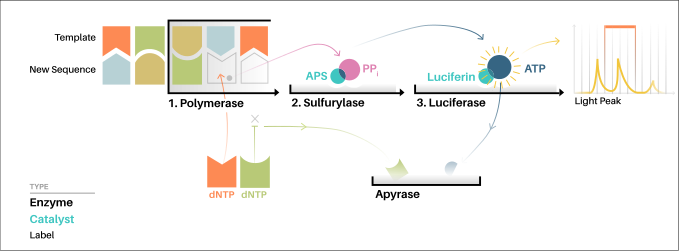
„Sekwencjonowanie przez syntezę” obejmuje pobranie pojedynczej nici DNA do sekwencjonowania, a następnie enzymatyczną syntezę jej komplementarnej nici. Metoda pirosekwencjonowania polega na wykrywaniu aktywności polimerazy DNA (enzymu syntetyzującego DNA) z innym enzymem chemoluminescencyjnym . Zasadniczo metoda ta umożliwia sekwencjonowanie pojedynczej nici DNA poprzez syntezę komplementarnej nici wzdłuż niej, po jednej parze zasad na raz i wykrywanie, która zasada została faktycznie dodana na każdym etapie. Matrycowy DNA jest nieruchomy, a roztwory nukleotydów A, C, G i T są kolejno dodawane i usuwane z reakcji. Światło jest wytwarzane tylko wtedy, gdy roztwór nukleotydów uzupełnia pierwszą niesparowaną zasadę szablonu. Sekwencja roztworów, które wytwarzają sygnały chemiluminescencyjne, pozwala na określenie sekwencji matrycy.
W przypadku wersji Pyrosequencing opartej na roztworze, matryca jednoniciowego DNA ( ssDNA ) jest hybrydyzowana ze starterem do sekwencjonowania i inkubowana z enzymami polimerazą DNA , sulfurylazą ATP , lucyferazą i apyrazą oraz z substratami fosfosiarczanu adenozyny 5´ (APS) i lucyferyna .
- Dodanie jednego z czterech trifosforanów deoksynukleotydów ( dNTP ) (dATPαS, który nie jest substratem dla lucyferazy, dodaje się zamiast dATP, aby uniknąć szumu) inicjuje drugi etap. Polimeraza DNA wprowadza do matrycy prawidłowe, komplementarne dNTP. Ta inkorporacja uwalnia pirofosforan (PPi).
- Sulfurylaza ATP przekształca PPi w ATP w obecności fosfosiarczanu adenozyny 5 '. Ten ATP działa jako substrat do konwersji lucyferyny do oksylucyferyny, w której pośredniczy lucyferaza, która generuje światło widzialne w ilościach, które są proporcjonalne do ilości. Światło wytwarzane w reakcji katalizowanej lucyferazą jest wykrywane przez kamerę i analizowane w programie.
- Niewłączone nukleotydy i ATP są degradowane przez apyrazę i reakcja może zostać wznowiona z innym nukleotydem.
Proces można przedstawić za pomocą następujących równań:
- PPi + APS → ATP + siarczan (katalizowany przez ATP-sulfurylazę);
- ATP + lucyferyna + O2 → AMP + PPi + oksylucyferyna + CO2 + hv (katalizowana przez lucyferazę);
gdzie:
- PPi to pirofosforan
- APS oznacza 5-fosfosiarczan adenozyny;
- ATP to trifosforan adenozyny;
- O2 to cząsteczka tlenu;
- AMP to monofosforan adenozyny;
- CO2 to dwutlenek węgla;
- hv jest lekki.
Ograniczenia
Obecnie ograniczeniem metody jest to, że długości poszczególnych odczytów sekwencji DNA są bliskie 300-500 nukleotydów, czyli mniej niż 800-1000 możliwych do uzyskania metodami terminacji łańcucha (np. Sekwencjonowanie Sangera). Może to utrudnić proces składania genomu , szczególnie w przypadku sekwencji zawierających dużą ilość powtarzalnego DNA . Brak czynności korektorskich ogranicza dokładność tej metody.
Komercjalizacja
Firma Pyrosequencing AB w Uppsali w Szwecji została założona dzięki kapitałowi wysokiego ryzyka dostarczonemu przez HealthCap w celu komercjalizacji maszyn i odczynników do sekwencjonowania krótkich odcinków DNA przy użyciu techniki pirosekwencjonowania. Pyrosequencing AB została notowana na Sztokholmskiej Giełdzie Papierów Wartościowych w 1999 roku . W 2003 roku została przemianowana na Biotage . Linia biznesowa pyrosequencing została przejęta przez Qiagen w 2008 roku. Ponadto licencję na technologię Pyrosequencing otrzymało 454 Life Sciences . 454 opracował technologię pirosekwencjonowania opartą na macierzach, która wyłoniła się jako platforma do sekwencjonowania DNA na dużą skalę , w tym sekwencjonowania genomu i metagenomiki .
Roche ogłosił zaprzestanie produkcji platformy sekwencjonowania 454 w 2013 roku, kiedy jej technologia stała się niekonkurencyjna.
Bibliografia
Dalsza lektura
- Metzker M. (2005). „Nowe technologie w sekwencjonowaniu DNA” . Badania genomu . 15 (12): 1767–76. doi : 10,1101 / gr . 3770505 . PMID 16339375 .