Syntaza monofosforanu urydyny - Uridine monophosphate synthase
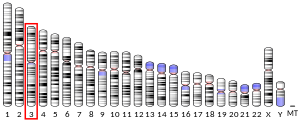
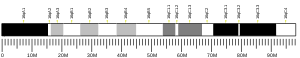
Syntaza monofosforanu urydyny ( UMPS ) ( transferaza fosforybozylowa orotanu i 5'-dekarboksylaza orotydyny ) jest enzymem katalizującym tworzenie monofosforanu urydyny (UMP), cząsteczki przenoszącej energię w wielu ważnych szlakach biosyntezy. U ludzi gen kodujący ten enzym znajduje się na długim ramieniu chromosomu 3 (3q13).
Struktura i funkcja
Ten dwufunkcyjny enzym ma dwie główne domeny, podjednostkę fosforybozylotransferazy orotanowej (OPRTaza, EC 2.4.2.10 ) i podjednostkę dekarboksylazy orotydyno-5'-fosforanowej (ODCaza, EC 4.1.1.23 ). Te dwa miejsca katalizują ostatnie dwa etapy szlaku biosyntezy de novo monofosforanu urydyny (UMP). Po dodaniu rybozy-P do orotanu przez OPRTazę z wytworzeniem orotydyno-5'-monofosforanu (OMP), OMP jest dekarboksylowany przez ODCazę do monofosforanu urydyny. W mikroorganizmach te dwie domeny są oddzielnymi białkami, ale u wielokomórkowych eukariontów dwa miejsca katalityczne ulegają ekspresji w pojedynczym białku, syntazie monofosforanu urydyny.
UMPS występuje w różnych formach, w zależności od warunków zewnętrznych. In vitro monomeryczny UMPS o współczynniku sedymentacji S 20,w 3,6 stanie się dimerem, S 20,w = 5,1 po dodaniu anionów, takich jak fosforan. W obecności OMP, produktu OPRTazy, dimer zmienia się w szybciej sedymentującą formę S 20,w 5.6. Te oddzielne formy konformacyjne wykazują różne aktywności enzymatyczne, przy czym monomer syntazy UMP wykazuje niską aktywność dekarboksylazy, a tylko dimer 5,6S wykazuje pełną aktywność dekarboksylazy.
Uważa się, że dwa oddzielne miejsca katalityczne połączyły się w jedno białko, aby ustabilizować jego formę monomeryczną. Związek kowalencyjny w UMPS stabilizuje domeny zawierające odpowiednie centra katalityczne, poprawiając jego aktywność w organizmach wielokomórkowych, w których stężenia mają tendencję do występowania 1/10 odrębnych odpowiedników u prokariotów. Inne mikroorganizmy z odseparowanymi enzymami muszą zachować wyższe stężenia, aby utrzymać swoje enzymy w bardziej aktywnej formie dimerycznej.
Połączenie
Zdarzenia fuzji OPRTazy i ODCazy, które doprowadziły do powstania dwufunkcyjnego enzymu UMPS, wystąpiły wyraźnie w różnych gałęziach drzewa życia. Po pierwsze, chociaż OPRTase znajduje się na N -końcu i ODCase na C -końcu, w większości organizmów eukariotycznych (np Metazoa, Amoebozoa, Plantae i Heterolobosea) odwróconej fusion to znaczy OPRTase na C - Wykazano również istnienie końca i ODCazy na końcu N (np. pasożytnicze protisty, trypanosomastidy i stramenopiles). Ponadto inne grupy eukariotyczne, takie jak grzyby, konserwują oba enzymy jako oddzielne białka.
Jakkolwiek ważna jest kolejność fuzji, ewolucyjne pochodzenie każdej domeny katalitycznej w UMPS jest również przedmiotem badań. Zarówno OPRTaza, jak i ODCaza przeszły przez boczne przeniesienie genów, w wyniku czego eukariota mają enzymy pochodzenia bakteryjnego i eukariotycznego. Na przykład Metazoa, Amoebozoa, Plantae i Heterolobosea mają eukariotyczną ODCazę i OPRTazę, podczas gdy Alveolata i stramenopiles mają bakteryjne. Możliwe są również inne rearanżacje, ponieważ grzyby mają bakteryjną OPRTazę i eukariotyczną ODCazę, podczas gdy kinetoplastydy mają odwrotną kombinację.
Łącząc zarówno kolejność fuzji, jak i pochodzenie ewolucyjne, organizmy dokonują fuzji UMPS, w której jedna z jej domen katalitycznych pochodzi od bakterii, a druga od eukariontów.
Siłą napędową tych zdarzeń fuzji wydaje się być uzyskana stabilność termiczna. Aktywności OPRTazy i ODCazy Homo sapiens są niższe po podgrzaniu w większym stopniu niż białko fuzyjne.
Aby określić siłę napędową asocjacji białek, przeprowadzono kilka eksperymentów, oddzielając obie domeny i zmieniając peptyd łącznikowy, który utrzymuje je razem. W Plasmodium falciparum kompleks OPRTaza-OMPDCase zwiększa stabilność kinetyczną i termiczną w porównaniu z enzymami jednofunkcyjnymi. U H. sapiens , chociaż oddzielne i połączone domeny mają podobną aktywność, te pierwsze mają wyższą wrażliwość na warunki sprzyjające dysocjacji monomeru. Ponadto peptyd łącznikowy można usunąć bez inaktywacji katalizy. W Leishmania donovani oddzielna OPRTaza nie ma wykrywalnej aktywności, prawdopodobnie z powodu niższej stabilności termicznej lub braku jej peptydu łącznikowego.
Rozporządzenie
UMPS podlega złożonej regulacji ze strony OMP, produktu jej OPRTazy i substratu dla ODCazy. OMP jest allosterycznym aktywatorem aktywności dekarboksylazy OMP. Przy niskim stężeniu enzymu i niskim stężeniu OMP, dekarboksylaza OMP wykazuje negatywną kooperację, natomiast przy wyższych stężeniach OMP enzym wykazuje pozytywną kooperację. Jednak gdy stężenia enzymów są wyższe, ta złożona kinetyka nie ujawnia się. Aktywność PRTazy orotanu jest aktywowana przez niskie stężenia OMP, fosforanów i ADP.
Mechanizm
OPRTase
OPRTaza P. falciparum podąża losowym szlakiem w syntezie i degradacji OMP. W analizach stanu przejściowego wykorzystano efekty izotopowe i obliczenia kwantowe, aby ujawnić całkowicie zdysocjowaną dianionową strukturę orotanu, rybokację i nukleofilową cząsteczkę pirofosforanu. Niemniej jednak jest to nieoczekiwane, ponieważ większość N-rybozylotransferaz obejmuje protonowane i obojętne grupy opuszczające, podczas gdy deprotonowany orotan nie jest dobry w kationowym stanie przejściowym.
OPRTase, jako członek PRTase typu I, ma wyraźną pętlę obok swojego aktywnego miejsca. Jest elastyczny w stanie otwartym i prawie nie można go zobaczyć na elektronicznych mapach gęstości dla niektórych OPRTase. Aby zaszła kataliza, musi istnieć dimer, w którym pętla z jednej podjednostki pokrywa miejsce aktywne z drugiej. U Salmonella typhimurium tworzona jest nowa para antyrównoległych β-kartek i pięć nowych kontaktów międzyatomowych powstaje w pętli, między pętlą a resztą białka oraz między pętlą a ligandami.
Jeśli chodzi o ruch pętli, istnieją dwie możliwości: może poruszać się w sposób sztywny lub może pochodzić z nieuporządkowanej struktury, która nabiera porządku. Drugi scenariusz wydaje się bardziej prawdopodobny w przypadku OPRTase. Musi istnieć równowaga energetyczna między nowym porządkiem peptydu a tworzeniem wiązań wodorowych w pętli, między pętlą a resztą białka oraz między pętlą a ligandami. Istnieje równowaga 30:1 pomiędzy strukturą zamkniętą i otwartą w kompleksie enzym-Mg-PRPP, co sugeruje, że preferowana jest bliska konformacja.
Resztom pętli katalitycznej zaproponowano różne role. Przede wszystkim wydaje się, że istnieje korelacja między ruchem pętli a położeniem katalizatora substratu. W reakcji biologicznej przeniesienie protonu na cząsteczkę pirofosforanu (PPi) może zminimalizować akumulację ładunku ujemnego, mimo że pKa dla PPi wynosi 9. Lys26, His105 i Lys103 są kandydatami do tego przeniesienia na pozycję α-fosforanu. Jednak może tak nie być, ponieważ łańcuchy boczne i jon metalu mogą zneutralizować część ładunku ujemnego z wytworzonego PPi. Stabilizację geometryczną stanu przejściowego można również uzyskać poprzez udział pętli.
ODCase
Callahan i Miller (2007) podsumowują mechanizmy ODCase w trzech propozycjach. Pierwszym z nich jest aktywacja karboksylu substratu poprzez stres elektrostatyczny. Wiązanie grupy fosforylowej pociąga za sobą zestawienie pomiędzy grupą karboksylanową i ujemnie naładowaną resztą Asp (mianowicie Asp91 w Saccharomyces cerevisae). Odpychanie między ładunkami ujemnymi podniosłoby wartość energii w pobliżu stanu przejściowego. Niemniej jednak analizy krystalograficzne i brak powinowactwa enzymu S. cerevisae do analogów substratu, w których grupy karboksylanowe zastąpiono podstawnikiem kationowym, wykazały pewne dowody przeciwko tej teorii.
Rozważano również protonowanie OMP na O4 lub O2 przed dekarboksylacją, która pociąga za sobą tworzenie ylidu na N1. Brak donora protonów w pobliżu O4 lub O2 w strukturach krystalograficznych jest dowodem przeciwko temu, wraz z wykluczeniem generowania ylidu jako etapem ograniczającym w eksperymentach 15N. Ponadto pojawiły się wątpliwości co do pośredniej żywotności protonowanej z powodu braku stabilizatorów elektronicznych. W konsekwencji zaproponowano zerwanie wiązania między C6 i C7 z powodu protonowania tego pierwszego przechodzącego przez stan karboanionowy.
Wreszcie kataliza może zachodzić przez proste przyciąganie elektrostatyczne. Tworzenie się karboanionów C6 spowodowałoby interakcje dipolowe z kationową Lys z miejsca aktywnego. Nie wyjaśnia to wzrostu prędkości w porównaniu z procesem niekatalizowanym.
Znaczenie kliniczne
Niedobór syntazy UMP może skutkować zaburzeniem metabolicznym zwanym kwasicą jamy ustnej .
Niedobór tego enzymu jest dziedziczną cechą autosomalną recesywną u bydła rasy holsztyńskiej i powoduje śmierć przed urodzeniem.
Niedobór tego enzymu można badać w organizmie modelowym Caenorhabditis elegans . Rad-6 szczep przedwczesny kodon stop eliminuje dekarboksylazy orotydyno-5'-domeny białka; domena ta nie występuje w żadnych innych białkach kodowanych przez genom. Szczep ma fenotyp plejotropowy, w tym zmniejszoną żywotność i płodność, powolny wzrost i wrażliwość na promieniowanie.
Znaczenie farmakologiczne
Wykazano, że UMPS i jego dwie oddzielne domeny, ODCaza i OPRTaza, mają zasadnicze znaczenie dla żywotności pasożytów z taksonu Chromoalveolata, takich jak L. donovani lub P. falciparum . Ponieważ UMPS, ODCaza i OPRTaza różnią się między organizmami, przeprowadzono badania nad inhibitorami specyficznymi dla gatunku.
Zahamowanie
OPRTase
Badania nad hamowaniem OPRTazy oparte są na analogach substratów. W przypadku Mycobacterium tuberculosis dwoma najbardziej obiecującymi inhibitorami są kwas 2,6-dihydroksypirydyno-4-karboksylowy i kwas 3-benzylideno-2,6-diokso-1,2,3,6-tetrahydropirydyno-4-karboksylowy. Entalpia Unii i entropia z tego ostatniego odpowiadają ligandom o wysokim powinowactwie. Badane są właściwości, takie jak lipofilność, rozpuszczalność, przepuszczalność i stałe równowagi.
Zastosowano również produkty selenacyjne. Abdo i in. (2010) przeprowadzili reakcje na kwasie 2-etoksyetanoselenowym z wykorzystaniem bogatych w elektrony aromatycznych substratów w celu wytworzenia eterów (2-etoksyetylo)seleno. Mogą one stać się produktami selenowanymi arylami, takimi jak rodzina 5-urydynylów, która wykazuje hamowanie w stężeniach submikromolarnych u P. falciparum i H. sapiens .
ODCase
Inhibitory ODCazy pochodzą również z analogów substratów, takich jak modyfikacje pierścieni OMP lub UMP. U H. sapiens ODCaza była hamowana przez związki halogenkowe pochodzące z UMP (np. 5-FUMP, 5-BrUMP, 5-IUMP i 6-IUMP.)
W przypadku Methanobacterium thermoautotrophicum zastosowano inną strategię, modyfikując słabo oddziałujące ligandy, takie jak cytydyno-5'-monofosforan, który jest pochodną barbituranu rybonukleozydo-5'-monofosforan, ksantozyno-5'-monofosforan. ODCaza P. falciparum została skutecznie zahamowana przez modyfikacje cytydyno-5'-monofosforanu N3 i N4.
Interaktywna mapa ścieżek
Kliknij poniżej geny, białka i metabolity, aby połączyć się z odpowiednimi artykułami.
Zobacz też
Bibliografia
Dalsza lektura
- Suchi M, Harada N, Tsuboi T, Asai K, Okajima K, Wada Y, Takagi Y (1990). „Klonowanie molekularne ludzkiej syntazy UMP”. Metabolizm puryn i pirymidyn u człowieka VI . Postępy w medycynie eksperymentalnej i biologii . 253A . s. 511-8. doi : 10.1007/978-1-4684-5673-8_83 . Numer ISBN 978-1-4684-5675-2. PMID 2624233 .
- Suttle DP, Bugg BY, Winkler JK, Kanalas JJ (marzec 1988). „Klonowanie molekularne i sekwencja nukleotydów dla całego regionu kodującego ludzką syntazę UMP” . Materiały Narodowej Akademii Nauk Stanów Zjednoczonych Ameryki . 85 (6): 1754–8. Kod Bib : 1988PNAS...85.1754S . doi : 10.1073/pnas.85.6.1754 . PMC 279857 . PMID 3279416 .
- Patterson D, Jones C, Morse H, Rumsby P, Miller Y, Davis R (maj 1983). „Strukturalny gen kodujący wielofunkcyjne białko przenoszące aktywność fosforybozylotransferazy orotanowej i dekarboksylazy OMP znajduje się na długim ramieniu ludzkiego chromosomu 3”. Genetyka komórki somatycznej . 9 (3): 359–74. doi : 10.1007/BF01539144 . PMID 6574608 . S2CID 29498380 .
- McClard RW, Black MJ, Livingstone LR, Jones ME (wrzesień 1980). „Izolacja i wstępna charakterystyka pojedynczego polipeptydu, który syntetyzuje 5'-monofosforan urydyny z orotanu w raku puchlinowym Ehrlicha. Oczyszczanie przez tandemową chromatografię powinowactwa syntazy urydyno-5'-monofosforanowej”. Biochemia . 19 (20): 4699-706. doi : 10.1021/bi00561a024 . PMID 6893554 .
- Iannuzzi L, Di Meo GP, Ryan AM, Gallagher DS, Ferrara L, Womack JE (maj 1994). „Lokalizacja genu syntazy monofosforanu urydyny (UMPS) do chromosomów rzecznych bawołów przez FISH”. Badania chromosomów . 2 (3): 255–6. doi : 10.1007/BF01553326 . PMID 8069469 . S2CID 13407149 .
- Ichikawa W, Uetake H, Shirota Y, Yamada H, Takahashi T, Nihei Z, Sugihara K, Sasaki Y, Hirayama R (październik 2003). „Zarówno ekspresja genów dla fosforybozylotransferazy orotanowej, jak i jej stosunek do dehydrogenazy dihydropirymidynowej wpływają na wynik po chemioterapii opartej na fluoropirymidynie w przypadku przerzutowego raka jelita grubego” . Brytyjski Dziennik Raka . 89 (8): 1486–92. doi : 10.1038/sj.bjc.6601335 . PMC 2394351 . PMID 14562021 .
- Miyoshi Y, Uemura H, Ishiguro H, Kitamura H, Nomura N, Danenberg PV, Kubota Y (2005). „Ekspresja syntazy tymidylanowej, dehydrogenazy dihydropirymidynowej, fosforylazy tymidynowej i fosforybozylotransferazy orotanowej w raku prostaty” . Rak prostaty i choroby prostaty . 8 (3): 260-5. doi : 10.1038/sj.pcan.4500817 . PMID 15999119 .
- Ochiai T, Sugitani M, Nishimura K, Noguchi H, Okada T, Ouchi M, Yamada M, Kitajima M, Tsuruoka Y, Takahashi Y, Futagawa S (październik 2005). „Wpływ orotanowej aktywności transferazy fosforybozylowej jako predyktora przerzutów do węzłów chłonnych w raku żołądka”. Raporty onkologiczne . 14 (4): 987–92. doi : 10.3892/lub.14.4.987 . PMID 16142362 .
- Stelzl U, Worm U, Lalowski M, Haenig C, Brembeck FH, Goehler H, Stroedicke M, Zenkner M, Schoenherr A, Koeppen S, Timm J, Mintzlaff S, Abraham C, Bock N, Kietzmann S, Goedde A, Toksöz E , Droege A, Krobitsch S, Korn B, Birchmeier W, Lehrach H, Wanker EE (wrzesień 2005). „Ludzka sieć interakcji białko-białko: zasób do opisywania proteomu”. Komórka . 122 (6): 957–68. doi : 10.1016/j.cell.2005.08.029 . hdl : 11858/00-001M-0000-0010-8592-0 . PMID 16169070 . S2CID 8235923 .
- Kitajima M, Takata N, Hata M, Maeda T, Sakamoto K, Kamano T, Ochiai T (styczeń 2006). „Związek między wrażliwością na 5-fluorouracyl a polimorfizmami pojedynczego nukleotydu genu fosforybozylotransferazy orotanowej w raku jelita grubego”. Raporty onkologiczne . 15 (1): 161–5. doi : 10.3892/lub.15.1.161 . PMID 16328050 .
- Ichikawa W, Takahashi T, Suto K, Sasaki Y, Hirayama R (lipiec 2006). „Polimorfizm genu fosforybozylotransferazy orotanowej przewiduje toksyczność u pacjentów leczonych bolusem 5-fluorouracylowym w schemacie” . Kliniczne badania nad rakiem . 12 (13): 3928–34. doi : 10.1158/1078-0432.CCR-05-2665 . PMID 16818689 .
- Taomoto J, Yoshida K, Wada Y, Tanabe K, Konishi K, Tahara H, Fukushima M (2007). „Nadekspresja genu orotanu fosforybozylotransferazy wzmacnia działanie 5-fluorouracylu na linie komórkowe raka żołądka”. Onkologia . 70 (6): 458–64. doi : 10.1159/000098873 . PMID 17237621 . S2CID 8032104 .
- Nio Y, Toga T, Maruyama R, Fukushima M (lipiec 2007). „Ekspresja orotanowej transferazy fosforybozylowej w ludzkim raku trzustki: implikacje dla skuteczności chemioterapii adiuwantowej opartej na uracylu i tegafurze” . Raporty onkologiczne . 18 (1): 59–64. doi : 10.3892/lub.18.1.59 . PMID 17549346 .
- Sanada Y, Yoshida K, Ohara M, Tsutani Y (2007). „Ekspresja orotanowej fosforybozylotransferazy (OPRT) w raku wątroby i trzustki”. Patologia i badania onkologiczne . 13 (2): 105–13. CiteSeerX 10.1.1.629.7176 . doi : 10.1007/BF02893485 . PMID 17607371 . S2CID 32129544 .
- Sakamoto E, Nagase H, Kobunai T, Oie S, Oka T, Fukushima M, Oka T (listopad 2007). „Poziom ekspresji fosforybozylotransferazy orotanowej w nowotworach jest potencjalnym wyznacznikiem skuteczności 5-fluorouracylu”. Komunikacja badań biochemicznych i biofizycznych . 363 (1): 216–22. doi : 10.1016/j.bbrc.2007.08.164 . PMID 17854773 .